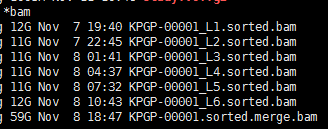
有这个需求,是因为我们经常对某些细胞系进行有针对性的设计变异,比如BAF155的R1064K呀,H3F3A的K27呀,那我我们拿到高通量测序数据的时候,就肯定希望可以快速的看看这个基因是否被突变成功了。现在比对几乎不耗费什么时间了,但是得到的sam要sort的时候还是蛮耗费时间的。假设,我们已经得到了所有样本的sort好的bam文件,想看看自己设计的基因突变是否成功了,可以有针对性的只call 某个基因的突变!
Monthly Archives: 11月 2016
仔细探究picard的MarkDuplicates 是如何行使去除PCR重复reads功能的
本帖紧跟前面的仔细探究samtools的rmdup是如何行使去除PCR重复reads功能的
同样的我们也是分单端和双端测序来看结果,并且比较两个工具的区别!
首先对于那个单端数据,samtools给出的结果是:[bam_rmdupse_core] 25 / 53 = 0.4717 in library Continue reading
仔细探究samtools的rmdup是如何行使去除PCR重复reads功能的
数据库批量注释不可盲目-annovar数据库错误
我对H3F3A这个基因做了两个突变的cellline,分别是G34V和K27M,现在知道这个基因在hg38上面的坐标是:
Genomic Location for H3F3A Gene
Chromosome: 1
Start:226,061,851 bp from pter End:226,072,002 bp from pter
Size:10,152 bases Orientation:Plus strand
然后我用samtools结合bcftools把该基因区域的snp位点call出来:
samtools mpileup -r chr1:226061851-226072001 -t "DP4" -ugf ~/reference/genome/hg38/hg38.fa *sorted.bam | bcftools call -vmO z -o H3F3A.vcf.gz
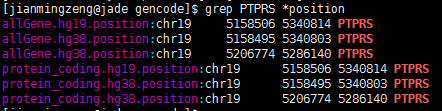
一个基因在同一套基因组上面竟然有两个定位!
查了好久的bug,终于搞清楚问题所在了!因为要对基因进行reads计数,所以要拿到基因在基因组上面的染色体起始终止坐标,结果发现了个十分诡异的现象,很多基因有多个坐标,比如下面这个PTPRS 在hg38这个基因组版本,居然有两个定位,因为我是写程序格式化得到的坐标,所以我check了我的程序,http://www.biotrainee.com/thread-472-1-1.html 感兴趣的同学可以点开看看我的代码!
mysql的table居然有最大列限制
【直播】我的基因组(五):测试数据及参考基因组的准备
我的全基因组数据还没拿到,而且还会推迟,简单说(tu)明(cao)一下原因(还好当初为了避免广告嫌疑一直没说是哪个公司负责测序,反正用的是illumina的hiseqX10这个测序啦,所以可以尽情的吐槽)。
心烦意乱的吐槽线 Continue reading
热图最佳实践-pheatmap
用pheatmap来绘图首先要安装这个包,它就一个功能,画出热图即可,号称是pretty heatmap,的确比其它的好用很多。我以前写过《一步一步学习heatmap.2》的教程,很简单的那种,所以就没有公布在博客上面,结果发现很多其它博客居然能先我一步发出。其实包括本次的pheatmap指南,都没什么好发,的在R里面也是傻瓜式出图,无法就是自己熟练一下参数而已,又不是开发一个包,没什么技术含量。我这里单独提一下pheatmap是因为它的确非常好用,将会是我画热图的不二之选。比如下面这个,是我最喜欢的: Continue reading