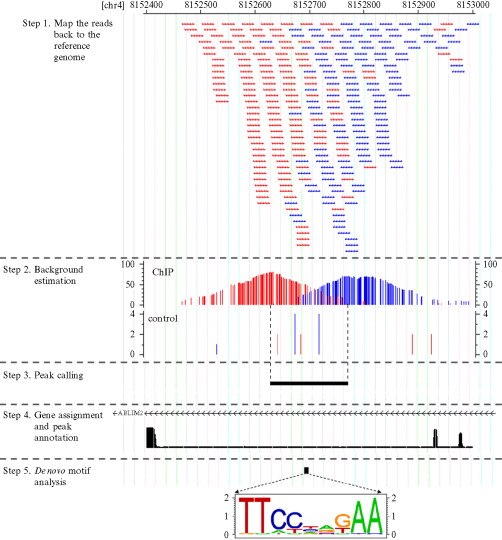
之前分析了好几个公共项目,拿到的peaks都很诡异,搞得我一直怀疑是不是自己分析错了。终于,功夫不负有心人,我分析了一个数据,它的peaks非常完美!!!可以证明,我的分析流程以及peaks绘图代码并没有错!数据来自于http://www.ncbi.nlm.nih.gov/geo/query/acc.cgi?acc=GSE74311,是关于H3K27ac_ChIP-Seq_LOUCY,组蛋白修饰的CHIP-seq数据,很容易就下载了作者上传的测序数据,然后跑了我的流程!https://github.com/jmzeng1314/NGS-pipeline/tree/master/CHIPseq Continue reading
八
02