下载软件
http://tree.bio.ed.ac.uk/software/figtree/
我们这里就在window平台下使用,所以直接下载zip包即可,解压即可使用
准备数据
我这里就简单的用muscle生成了一个树文件来看看结果TRAV.fa 是一百多个类似的基因
muscle -in TRAV.fa -out tmp
muscle -maketree -in tmp -out TRAV.tree
这个树文件TRAV.tree是Newick format,可以直接被figtree识别从而画图
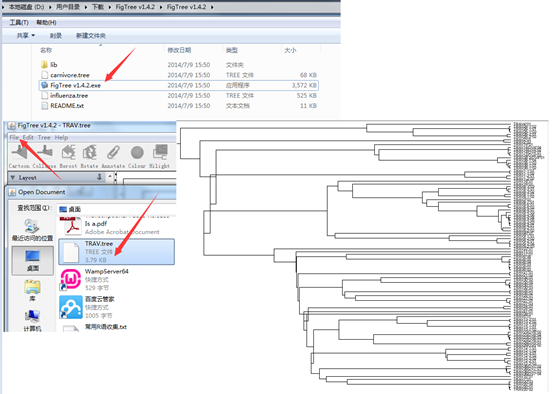
软件使用
很简单,下载,点击即可使用,然后导入树文件,就可以直接出图啦!