基因测序包括全基因组,全外显子组,以及捕获基因测序,不同技术研究的基因组范围不一样,都有自己合适的方向。还有另外一种分类是基于生物学应用,比如肿瘤外显子,家系外显子等等。
看到发表在2015年Journal of Human Genetics杂志的文章:Biotin-responsive basal ganglia disease: a case diagnosed by whole exome sequencing,链接是;https://www.nature.com/articles/jhg201535
研究者做了一个家系外显子,走的是GATK+ANNOVAR流程,测序家系如下:
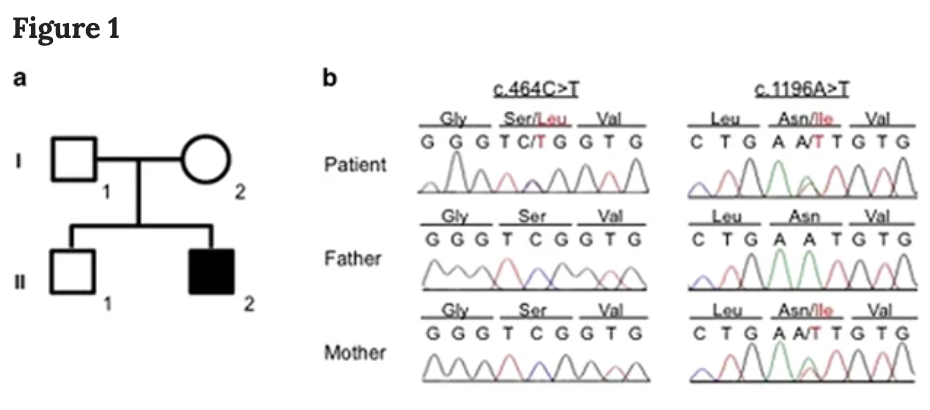
全外显子组基因测序结果,患儿94.4%的编码序列被至少20个reads(读长)覆盖。通过过滤41个BBGD或Leigh综合征已知疾病基因的变异体,确定了3个基因的4个变异。如下所示:
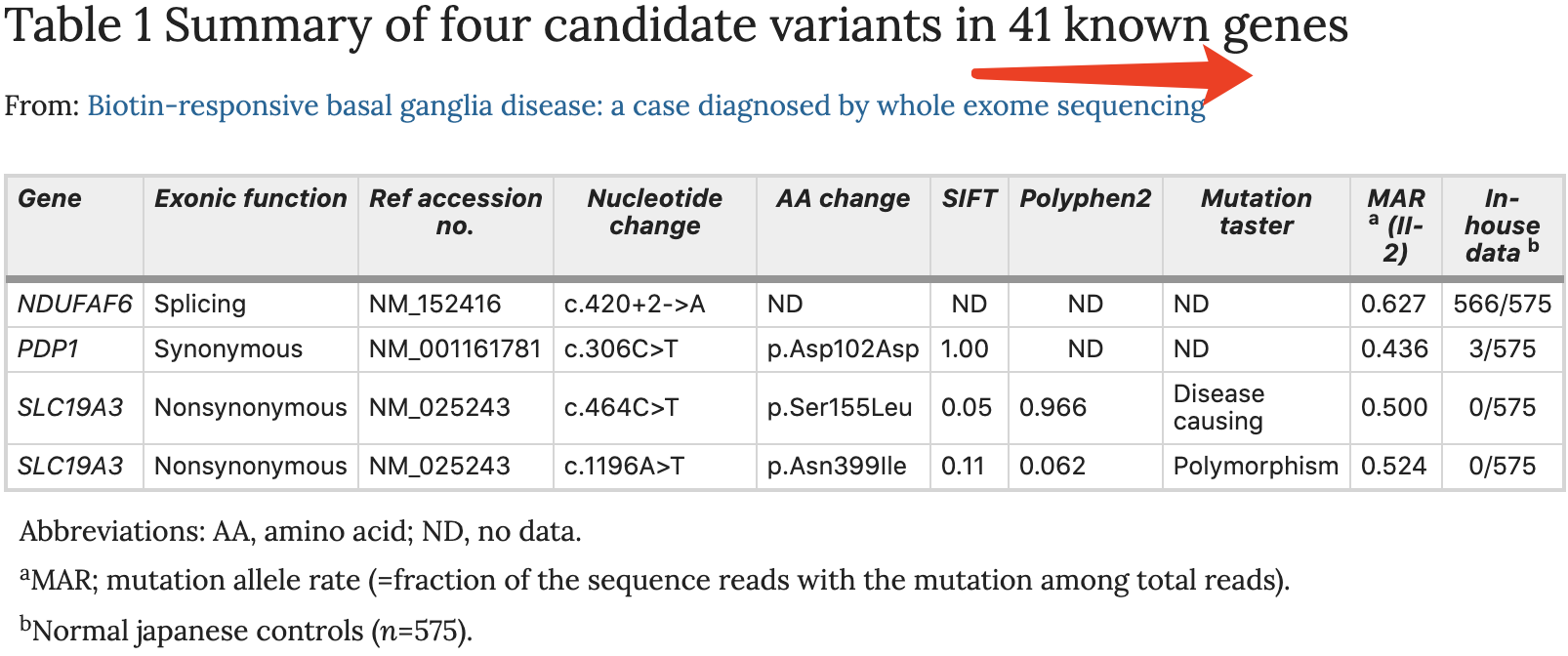
然后作者集中精力查询这4个变异:
- Among these variants, a synonymous variant in PDP1 (c.306C>T) and one splicing variant in NDUFAF6 (c.420+2->A), which was observed in 566 individuals of our in-house Japanese exome database (n=575), were excluded from the candidate variants.
- The remaining two heterozygous missense mutations were found in SLC19A3 (NM_025243.3): c.464C>T, p.Ser155Leu and c.1196A>T, p.Asn399Ile. SLC19A3 mutations are known to cause autosomal-recessive BBGD.
- These variants were not registered in our in-house exome database, 1000 Genomes database, or NHLBI Exome Sequencing Project (ESP6500).
- 其实也可以去迄今最大规模的人类遗传变异数据库gnomAD(https://gnomad.broadinstitute.org)看看这几个变异位点的详细情况。
实际上,这个课题用不上太多的生物信息学技术,因为家系收集是医院的事情,3个wes测序数据大部分科研服务公司都可以提供,也就是3000块钱左右啦,现在测序通常是赠送标准分析,比如GATK+ANNOVAR流程。每个人在外显子区域都有2万左右的变异位点。
然后查询疾病相关数据库,生物学背景知识啦。比如本文就是关心41个BBGD或Leigh综合征已知疾病基因的变异体,比较幸运的定位到了3个基因的4个变异。
但是,聪明的读者肯定看出来了,其实研究者并不需要全外显子组,因为反正最后也是仅仅能考虑41个BBGD或Leigh综合征已知疾病基因的变异体,大量的信息都是直接抛弃的!!!那么全基因组呢
既然2015已经做了全外显子组,后面的科学家就没办法搞一模一样的家系了,毕竟科学研究需要创新,这个时候可以选择扩大病人队列,或者做全基因组。
比如2019的文章,Targeted SLC19A3 gene sequencing of 3000 Saudi newborn: a pilot study toward newborn screening 就是超级大队列,而且仅仅是需要关心SLC19A3一个基因即可,成本优势很明显哦!
比如发表在 PLoS One. 2016; 的文章,Novel SLC19A3 Promoter Deletion and Allelic Silencing in Biotin-Thiamine-Responsive Basal Ganglia Encephalopathy ,里面的测序不少哦:WES in the two siblings revealed shared rare variants consistent with autosomal recessive inheritance in 7 genes, none of which had a known link to the phenotype.
WGS was performed in patient-2 at HudsonAlpha Institute for Biotechnology (Huntsville, AL) using paired-end 100nt sequencing on the Illumina HiSeq.
值得一提的是,这两个研究的文章里面都没有提供测序数据下载。提供临床项目咨询
大家可以看到,这样的课题,测序科研服务公司存在感很低,医院收集家系病人反而是项目主导,但是大量的医学科研人员并不能很好的处理这样的家系外显子数据个性化分析,可以考虑发邮件(jmzeng1314@163.com)咨询我,或者联系我微信。我的二维码在:0元,10小时教学视频直播《跟着百度李彦宏学习肿瘤基因组测序数据分析》,添加好友务必注明来意。